臭豆腐是中国传统的地方特色轻度发酵豆制品,历史悠久,“闻起来臭,吃起来香”是臭豆腐的显著特点。中国臭豆腐种类繁多,其中湖南长沙臭豆腐因其“黑如墨、香如醇、嫩如酥、软如绒”的特点而深受广大消费者喜爱。各地臭豆腐从原料和制作工艺都有所不同,而制作长沙臭豆腐需先制作臭卤水,再将制作好白豆腐浸泡进行轻度发酵,以获得含独特“臭味”的臭豆腐坯,再在低温冷链条件下运输到加工门面进行油炸食用。臭卤水是用豆豉、香菇、苋菜、竹笋和香辛料等植物为原料加水混合自然发酵数月至3年不等,使其具有特异的植物发酵液风味[1-5]。微生物在臭豆腐特殊风味的形成过程中起到至关重要的作用:臭豆腐卤水中原料的蛋白质被微生物分解为多肽及氨基酸,且释放出吲哚、苯酚等特殊风味的物质,油炸后挥发,从而形成了臭豆腐的特殊风味[6-8]。谷静思等[9]通过对臭豆腐高通量测序分析,共发现212种细菌,其中66种属于乳酸菌。贺静等[10]通过454高通量技术对臭豆腐卤水微生物多样性进行分析,发现不同样品优势菌种差异较大,说明卤水来源不同对微生物的差异显著。赵国忠等[11]通过传统微生物鉴定和16SrRNA对臭豆腐卤水微生物进行分析,分离鉴定出漫游球菌(Vagococcus carniphilus)、嗜冷杆菌属(Psychrobacter)、沙克乳杆菌(Lactobacillus sakei)、地衣芽孢杆菌(Enterococcus avium)、鸟肠球菌(Enterococcus devriesei)等细菌。谭金萍[12]则从卤水中分离与臭豆腐卤水风味成分密切相关的微生物环状芽孢杆菌(Bacillus circulans)和解硫胺素解硫胺素杆菌(Bacillus aneurinolyticus)。
目前对于臭豆腐的微生物研究大多集中在臭豆腐卤水,由于臭豆腐一般在企业生产半成品—臭豆腐生坯进行真空包装后再输送到连锁店进行油炸食用和产品推广,但因产品水分含量高,物流过程中冷链输送特别是高温季节稍有不慎就会出现产气涨包,影响产品质量甚至安全[6]。本实验以5个不同厂家的臭豆腐生坯为研究对象,通过高通量测序技术分析臭豆腐生坯中细菌多样性,并对其进行主成分分析(principal component analysis,PCA),探索出5种不同厂家臭豆腐生坯之间微生物多样性特点,为预防和控制半成品胀气提供重要参考,为产业链安全和质量保证奠定基础。
1 材料与方法
1.1 材料与试剂
1.1.1 材料
臭豆腐生坯(编号为YYD1、HSJD2、CGL3、PJX4、JXF5):来自5个不同生产企业用于流通领域的低温保存半成品(0~8 ℃)。
1.1.2 化学试剂
氢氧化钠、邻苯二甲酸氢钾(均为分析纯):国药集团化学试剂有限公司;酚酞溶液Phusion热启动Flex 2X预混液:上海仪涛生物仪器有限公司;DL2000脱氧核糖核酸(deoxyribonucleic acid,DNA)Marker:日本Takara公司;Qubit dsDNA HS Assay Kit:美国英杰生命技术有限公司;琼脂糖G-10:法国Biowest公司;50×TAE 缓冲液:上海生工生物工程股份有限公司;AxyPre聚合酶链式反应(polymerase chain reaction,PCR)清洁试剂盒:美国爱思进公司;RStool DNA试剂盒:美国Omega公司。
1.2 仪器与设备
LDZX-50 KBS高压蒸汽灭菌锅:上海申安医疗器械厂;SW-CJ-1FD无菌操作台:苏州净化设备有限公司;LRH-250生化培养箱:上海飞越实验仪器有限公司;S1000 PCR仪:美国BIO-RAD公司;MiSeq测序仪:美国Illumina公司;EPS 300型电泳仪、Tanon-2500型凝胶成像仪:上海天能公司。
1.3 试验方法
1.3.1 臭豆腐生坯样品基本指标测定
水分含量:按照GB 5009.3—2016《食品中水分的测定》;菌落总数:按照GB 4789.2—2016《菌落总数测定》;大肠菌群:按照GB 4789.3—2016《大肠菌群计数》。
1.3.2 臭豆腐生坯样品总DNA的提取
将臭豆腐生坯(YYD1、HSJD2、CGL3、PJX4、JXF5)与水按照质量比1∶9搅拌均匀后各取50 g,然后用孔径为0.22μm的水系微孔滤膜进行抽滤[13]。将抽滤完成后的滤膜剪碎放入微型离心管中,按照R Stool DNA试剂盒说明书提取总DNA。
1.3.3 臭豆腐生坯16S rDNA高通量测序方法
以臭豆腐生坯总DNA为模板进行细菌16S rDNA V3-V4区域扩增。引物:338F(ACTCCTACGGGAGGCAGCAG);806R(GGACTACHVGGGTWTCTAAT)。
PCR扩增体系:DNA模板50 ng、上下游引物各为2.5 μL、12.5 μL PCR预混合物、双蒸水25 μL。
PCR扩增条件:98 ℃预变性30 s;98 ℃变性10 s,54 ℃退火30 s,72 ℃延伸45 s,循环35次;最后72 ℃延伸10 min。
取PCR产物10 μL用2%琼脂糖凝胶电泳进行检测,将检测合格样品送至杭州联川生物技术有限公司进行高通量测序[14-15]。
1.3.4 数据分析
纯化后的样品由杭州联川生物有限公司进行上机测序。为了保证后续结果的可靠性,使用Vsearch(V2.3.4)软件过滤去除长度<100 bp的序列、含不确定碱基达5%以上的序列及嵌合体序列等低质量序列。再以平均邻近聚类算法通过Verseach(V2.3.4)将具有97%以上相似性的序列划分为同一个操作分类单(operational taxonomic units,OTU),挑选代表性序列使用[16-17]。在核糖体数据库项目(ribosomal database project,RDP)中进行序列比对,明确序列的分类地位。通过Alpha和Beta多样性分析研究单个样本中物种的多样性和多个样本间菌群结构的差异。对样品进行PCA,并基于16S rRNA基因扩因子测序结果作图。
1.3.5 数据处理
采用Origin 8.0、SPSS 18.0和Excel 2019进行数理统计分析和相关性分析。
2 结果与分析
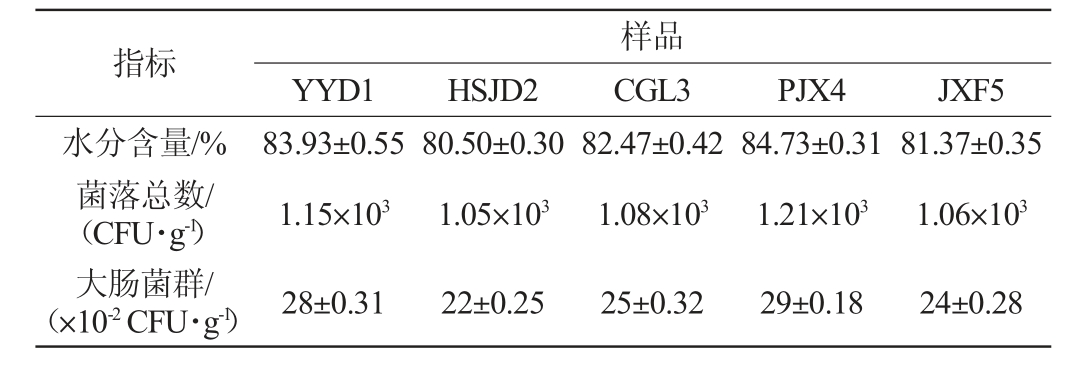
2.1 5种臭豆腐生坯样品基本指标测定结果
由表1可知,不同厂家臭豆腐生坯的水分、菌落总数和大肠菌群存在一定差异,这可能是加工工艺不同所导致的。在5种臭豆腐生坯中,样品PJX4水分含量、菌落总数、大肠菌群均最高,分别为84.73%、1.21×103 CFU/g、29×10-2 CFU/g;样品HSJD2水分含量、菌落总数、大肠菌群均最低,分别为80.50%、1.05×103 CFU/g、22×10-2 CFU/g。可能是水分含量与菌落总数和大肠菌群呈正相关。
表1 5种臭豆腐生坯样品基本指标检测结果
Table 1 Determination results of basic indexes of 5 kinds of stinky tofu Shengpei samples
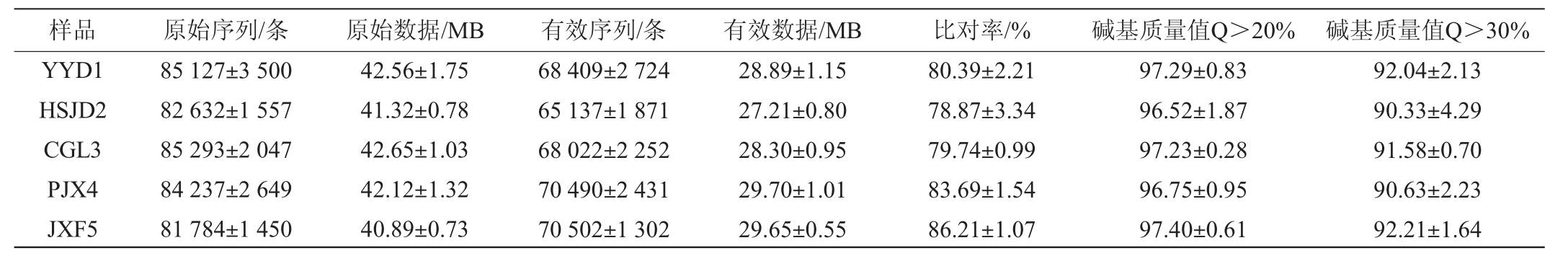
2.2 5种臭豆腐生坯样品测序数据统计分析
通过IlluminaMiSeq测序后5个样品共产生了1 676 294条有效数据(Valid Tags),本次测序有效数据统计结果见表2。
由表2可知,5种臭豆腐生坯样品中共得到342 560个有效的序列数(Tags)。5种样品中碱基质量值(Q>20%和Q>30%)的数据均在90%以上,表明此次测序数据较好,可进行后续数据分析。
表2 5种臭豆腐生坯样品测序有效数据统计
Table 2 Sequencing valid data statistics of 5 kinds of stinky tofu Shengpei samples
2.3 5种臭豆腐生坯样品Alpha多样性分析
Chao1指数曲线是反映样品微生物丰富度的指标,也可以用来说明样本的测序数据量是否合理。当曲线趋向平坦时,说明测序数据量合理,可以反映样品中绝大多数细菌的物种信息[18-19]。基于高通量测序技术对臭豆腐生坯细菌的Chao1指数进行分析,5种臭豆腐生坯样品Chao1指数曲线见图1。
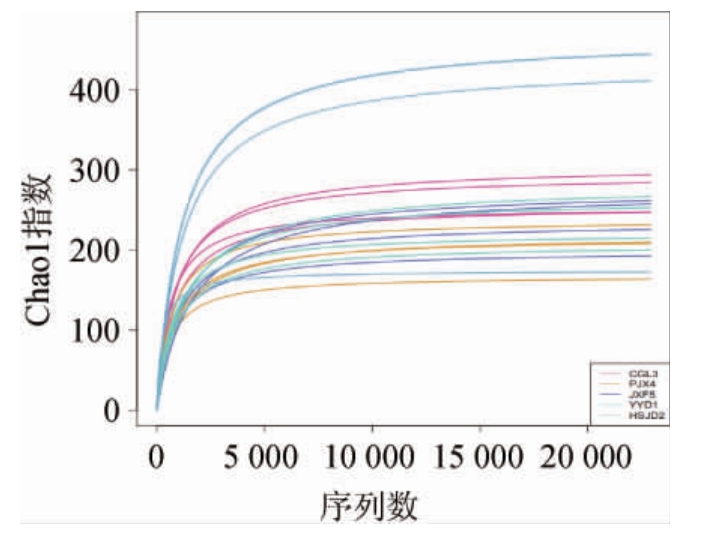
图1 5种臭豆腐生坯样品Alpha多样性分析结果
Fig.1 Alpha diversity analysis results of 5 kinds of stinky tofu Shengpei samples
从图1可以看出,随着序列数增加,样品的Chao1指数均值>150,说明5种样品的物种多样性和丰富度都较高。从样品重复性稀释曲线来看,在测序达到5 000以上基本趋于平缓,可以说明样品基本可以代表样品OTU实际情况,能够反映样品中微生物多样性丰富程度,可以评价覆盖所有微生物类群。
2.4 5种臭豆腐生坯样品的主成分分析
采用PCA对五个样品的多样性进行分析,评估其种群结构的差异性和相似性。结果如图2。由图2可知,PC1和PC2贡献率之和为87.21%。表明可以较好地反应各样品在图上的种群结构差异[20]。样品HSJD2、PJX4和YYD1距离较近,但是JXF5和CGL3距离较远。说明HSJD2、PJX4和YYD1菌群结构相似,而JXF5和CGL3与其他样品的菌群结构差异较大。
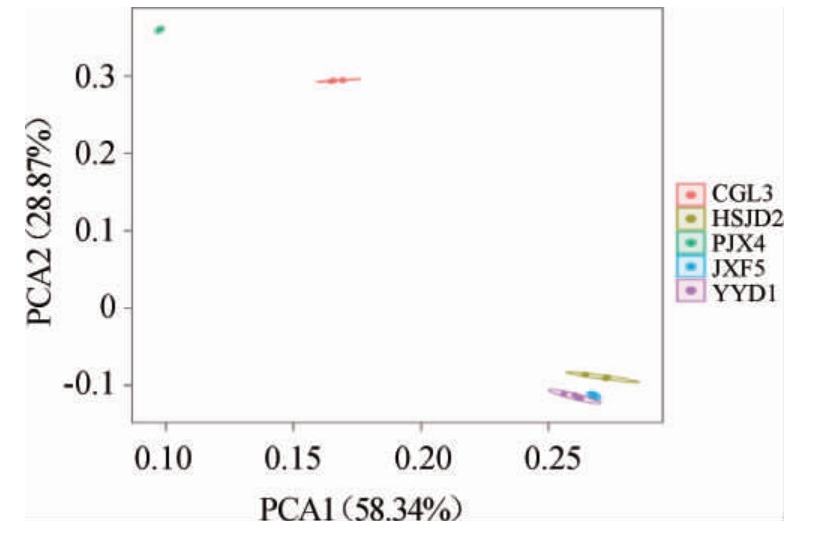
图2 5种臭豆腐生坯样品主成分分析结果
Fig.2 Principle component analysis results of 5 kinds of stinky tofu Shengpei samples
2.5 5种臭豆腐生坯样品中物种注释及分类
由图3可知,5种样品在门分类水平上共注释到30个门类。其中拟杆菌门(Bacteroidetes)和厚壁菌门(Firmicutes)总和在5种不同样品中均占80%以上占绝对优势,说明这5种不同的样品在门分类水平上有极大的相似性。拟杆菌门(Bacteroidetes)是肠道有益微生物,对膳食多糖有一定的降解作用[21]。其中ε-变形菌门(Epsilonbacteraeota)在样品CGL3相对丰度达4%,而在其他4个样品中相对丰度较少。而变形菌门(Proteobacteria)在样品YYD1、HSJD2和PJX4较多,分别为5%、3%和1%。在其他2种样品中相对丰度较少。综上,YYD1、HSJD2和PJX4样品相似且与样品CGL3和JXF5差异明显,与PCA结果相同。
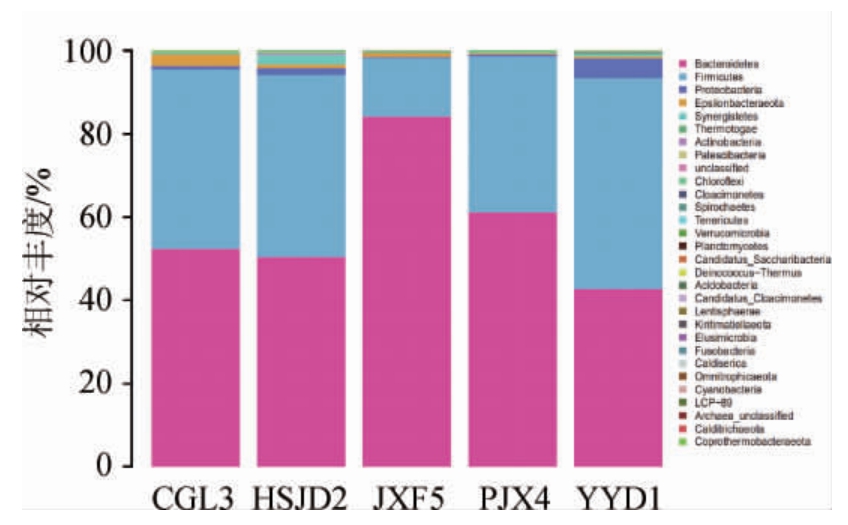
图3 5种臭豆腐生坯样品微生物群落门水平分类比较
Fig.3 Comparison of microbial community at phylum level classification of 5 kinds of stinky tofu Shengpei samples
由图4可知,在属分类水平上共注释到31个属类,普雷沃氏菌属(Prevotellaceae)在5种豆腐生坯样品中相对丰富均占绝对优势,特别是在JXF5中其相对丰度占70%以上。普雷沃氏菌属有降解碳水化合物和蛋白质的作用[22]。越来越多的研究表明,普雷沃氏菌属(Prevotellaceae)是有益的肠道微生物群,可以降解消化膳食多糖[23-24]。其次是梭菌属(Clostridium_sensu_stricto_13)和乳杆菌属(Lactobacillus)相对丰度较高。梭菌属(Clostridium_sensu_stricto_13)在样品CGL3的相对丰度超过15%,而乳杆菌属(Lactobacillus)在样品YYD1中相对丰度在20%以上。不同豆腐生坯微生物多样性的差异可能是卤水发酵过程中发酵不同的温度、pH值以及周围环境菌群所造成的影响。
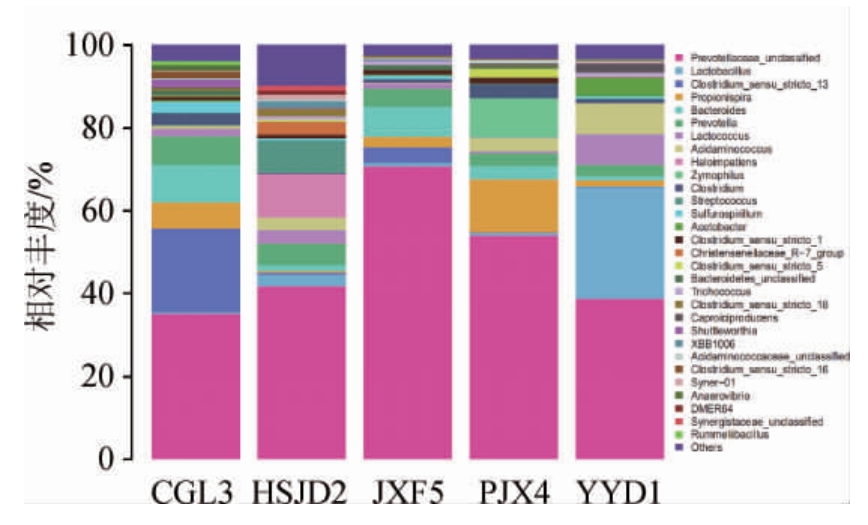
图4 5种臭豆腐生坯样品微生物群落属水平分类比较
Fig.4 Comparison of microbial community at genus level classification of 5 kinds of stinky tofu Shengpei samples
3 结论
本研究通过高通量测序测定5种不同厂家臭豆腐生坯,共注释到30个门类和31个属类。根据PCA发现,样品CGL3和JXF5差异较大。样品YYD1、HSJD2和PJX4较为相似。根据物种的门和属分类发现,拟杆菌门(Bacteroidetes)、厚壁菌门(Firmicutes)和普雷沃氏菌属(Prevotellaceae)在5种样品都占绝对优势,说明5种样品具有一定的相似性。普雷沃氏菌属和拟杆菌门在JXF5样品中相对丰度均>70%,两者都为肠道有益微生物,对膳食多糖具有降解功能,有望通过促进肠道健康,成为改善健康和预防疾病的功能性食品。综上所述,5种臭豆腐生坯中有益肠道的拟杆菌门和普雷沃氏菌属含量较高,而梭菌属和乳杆菌属含量又差异较大。普雷沃氏菌属大部分属于严格厌氧菌,大多数为革兰氏阴性细菌,而梭菌属和乳杆菌属属于革兰氏阳性细菌,为产气的嫌疑微生物,这有待于下一步采用纯培养方法将其中占据优势微生物进行分离纯化,鉴定其产气能力和水平,为进一步采用有效控制措施奠定科学依据。
[1]HAN B Z,ROMBOUTS F M,NOUT M J R.Amino acid profiles of sufu,a Chinese fermented soybean food[J]. J Food Compos Anal,2004,17(6):689-698.
[2]GU J S,LIU T J,SADIQ F A,et al.Biogenic amines content and assessment of bacterial and fungal diversity in stinky tofu-A traditional fermented soy curd[J].LWT-Food Sci Technol,2018,88:26-34.
[3]CHAO S H,TOMII Y,WATANABE K,et al.Diversity of lactic acid bacteria in fermented brines used to make stinky tofu[J].Int J Food Microbiol,2008,123(1-2):134-141.
[4]LIU T J,LI Y,SADIQ F A,et al.Predominant yeasts in Chinese traditionalsourdough and their influence on aroma formation in Chinese steamed bread[J].Food Chem,2018,242:404-411.
[5]顾渭忠.一种油炸臭豆腐中药卤汁的制作方法:CNl02018215A[P].2020-03-18.
[6]吴彩梅,王静,曹维强.臭豆腐的不安全因素及其监控[J].食品与发酵工业,2005,31(7):97-99,103.
[7] JANIASKI D R,PIMENTEL T C,CRUZ A G,et al.Strawberry-flavored yogurts and whey beverages:what is the sensory profile of the ideal product?[J].J Dairy Sci,2016,99(7):5273-5283.
[8] AGUIRRE L,HEBERT E M,GARRO M S,et al.Proteolytic activity of Lactobacillus strains on soybean proteins[J].LWT-Food Sci Technol,2014,59(2):780-785.
[9]谷静思,侯娟,何国庆.高通量测序分析臭豆腐中的细菌菌种多样性[J].中国食品学报,2019,19(3):250-255.
[10]贺静,谢靓,曾玉伦,等.454 高通量技术比较两种不同臭豆腐卤水中微生物多样性[J].微生物学杂志,2017,37(4):46-52.
[11]赵国忠,谢小芳,邸海波,等.臭豆腐卤水微生物群落及其接种发酵[J].中国酿造,2017,36(2):21-24.
[12]谭金萍.臭豆腐卤水中产苯酚菌的分离鉴定及应用[D].长沙:湖南农业大学,2019.
[13]周金沙,陈晓艺,谭金萍,等.基于Illumina MiSeq 高通量测序技术分析广西无盐发酵酸笋中细菌多样性[J].中国酿造,2019,38(7):85-90.
[14] CALLAHAN B J,MCMURDIE P J,ROSEN M J,et al.DADA2:Highresolution sample inference from Illumina amplicon data[J].Nat Methods,2016,13(7):581-583.
[15] BOLYEN E,RIDEOUT J R,DILLON M R,et al.Reproducible,interactive,scalable and extensible microbiome data science using QIIME 2[J].Nat Biotechnol,2019,37:852.
[16]ROGNES T,FLOURI T,NICHOLS B,et al.A versatile open source tool for metagenomics.Peer J,2016,4:e2584.
[17] LANGILLE M G I,ZANEVELD J,CAPORASO J G,et al.Predictive functional profiling of microbial communities using 16S rRNA marker gene sequences[J].Nat Biotechnol,2013,31:814-821.
[18]陈泽斌,李冰,徐胜光,等.高通量测序分析食用玫瑰花瓣内生细菌多样性[J].中国食品学报,2017,17(9):227-235.
[19]何理,吴晖.市售臭豆腐中菌种的分离及生化鉴定[J].现代食品科技,2012,28(8):952-955,958.
[20]张青,郭淑文,苏靖,等.基于高通量测序技术巴彦淖尔市酸粥中细菌多样性分析[J].中国酿造,2020,39(9):101-105.
[21] TIAN L M,BRUGGEMAN G,BERG M V D,et al.Effects of pectin on fermentation characteristics,carbohydrate utilization and microbial community composition in the gastrointestinal tract of weaning pigs[J].Mol Nutr Food Res,2016,61(1):1600186.
[22]张洁,张力莉,徐晓锋.反刍动物瘤胃内普雷沃氏菌的研究进展[J].中国饲料,2020(7):17-21.
[23] TIAN L M,SCHOLTE J,BOREWICZ K et al.Effects of pectin supplementation on the fermentation patterns of different structural carbohydrates in rats[J].Mol Nutr Food Res,2016,60(10):2256-2266.
[24]TIAN Y Z,LIU X,LIU W,et al.A new anti-proliferative acylated flavonol glycoside from Fuzhuan brick-tea[J].Nat Prod Res,2016,30(23):2637-2641.